|
patty82
Nuovo Arrivato

31 Messaggi |
 Inserito il - 15 giugno 2010 : 10:07:59 Inserito il - 15 giugno 2010 : 10:07:59




|
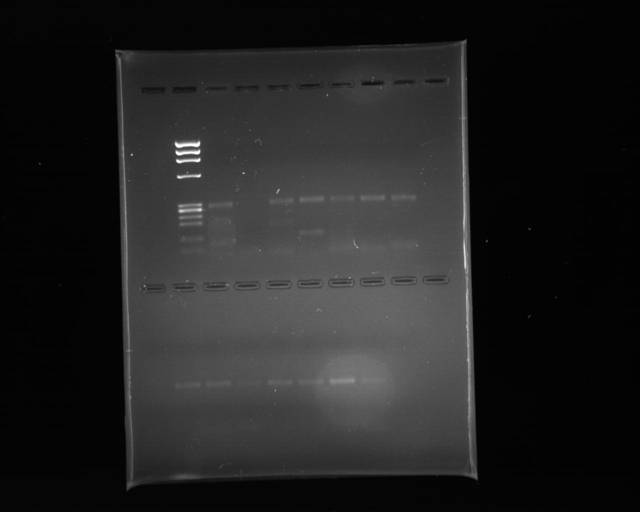
Buongiorno ragazzi sto analizzando dei polimorfismi all'interno del gene che codifica per i recettori degli androgeni mediante una tecnica che si chiama Humara. Questa tecnica consiste in diversi passaggi:
- digestione con due enzimi HpaII e HHaI
- pcr sia su dna digerito che sul non digerito
- sequenziamento
Per ora ho fatto digestione e pcr. Vi allego la foto del gel che ho fatto per controllare il risultato della pcr. Contate che l'amplificato che devo ottenere � di circa 300 bp e che i primers dovrebbero essere specifici per il gene e che la digestione la faccio sul dna genomico. Quello che volevo capire �: perch� oltre alla banda di 300 bp ne ottengo tante altre? E che differenza dovrei vedere tra il digerito e il non digerito? Insomma guardando la foto, voi cosa direste? Perch� poi io mi chiedo, se mando a sequenziare quello che ho ottenuto, essendoci altre bande e quindi altri frammenti di dna, non mi sequenzia anche quello?
Per la lettura della foto vi dico che, avendo fatto un test di ripetibilit�, i primi 10 campioni dopo il marker sono il mio dna digerito alla stessa concentrazione (25 ng) e successivamente amplificato mediante pcr. I due successivi sono sempre dna alla stessa concentrazione digerito allo stesso modo, ma fatto in una seduta analitica diversa; i due campioni subito dopo sono dei controlli, quindi dna alla stessa concentrazione ma non digerito e infine abbiamo un bianco che per fortuna � pulito.
Grazie mille attendo le vostre interpretazioni.
Immagine:
11,63 KB
|
|





