Quanto � utile/interessante questa discussione:
| Autore |
Discussione |
|
|
Donde
Utente Junior



272 Messaggi |
 Inserito il - 28 ottobre 2006 : 15:11:04 Inserito il - 28 ottobre 2006 : 15:11:04





|
Salve a tutti, devo dare l'esame di Chimica Fisica e sono abbastanza disperato. In particolare ho difficolt� a comprendere totalmente le assunzioni della fisica quantistica ed il calcolo con gli operatori.
Sapete dove posso trovare in rete qualcosa che spighi nel modo pi� chiaro possibili questi argomenti?
Grazie per l'aiuto...[V
|
"DNA just is. And we dance to its music." |
|
|
|
|
atreliu
Amministratore
  

Prov.: Milano
Citt�: Milano

2484 Messaggi |
 Inserito il - 28 ottobre 2006 : 22:55:20 Inserito il - 28 ottobre 2006 : 22:55:20








|
In effetti anche a me servirebbe del materiale (su descrittori quantomeccanici, in particolare): Korda sai darci una mano? O hai trovato materiale su Libri, etc.. e quali?
Ric |
MolecularLab.it - Animazioni, News, didattica & Community su bioinformatica, biologia molecolare ed ingegneria genetica.
BUONE REGOLE DEL FORUM:
- Prima di postare qualunque cosa leggere il Regolamento!
- Hai provato a cercare prima di postare il tuo problema? |
 |
|
|
kORdA
Utente Attivo
  

Prov.: Milano
Citt�: Monza

1303 Messaggi |
 Inserito il - 31 ottobre 2006 : 00:09:17 Inserito il - 31 ottobre 2006 : 00:09:17





|
Onestamente non sono molto pratico di quantomeccanica. Quando a me dicono che una macromolecola puo' essere semplificata e descritta attraverso un'oscillatore armonico classico tanto mi basta 
A parte gli scherzi, se pu� servire qui trovate la intro che avevo messo nella mia tesi (purtroppo ho dovuto ricorrere al solito sito di webhosting, non riesco a caricare nessun allegato qui). Un po' di teoria c'e' (piu' che altro potrebbe tornare utile la bibliografia).
Piu' di tanto non posso esserti utile Atreliu: i descrittori quantomeccanici vengono impiegati intensamente da chi fa ab-initio (non e' il mio caso). Per il momento ho confidato nella prassi di usare descrittori AM1 piuttosto che PM3 a seconda che dovessi ottimizzare la conformazione di un ligando aromatico o meno.
Ad ogni modo una buona guida erano i tutorial relativi al modulo AMPAC/MOPAC. Adesso che InsightII andra' in pensione per essere sotituito da Material Studio non so cosa mettera' a disposizione l'Accelrys come consultazione. |
http://www.linkedin.com/in/dariocorrada |
 |
|
|
atreliu
Amministratore
  

Prov.: Milano
Citt�: Milano

2484 Messaggi |
 Inserito il - 31 ottobre 2006 : 12:38:36 Inserito il - 31 ottobre 2006 : 12:38:36








|
Ho dato una occhiata agli Help di MOE e sono riuscito a trovare qualcosa ed anche pi�..
I descrittori sono valori che servono per descrivere numericamente e caratterizzare la molecola.
I descrittori si suddividono in classi:
# 2D. Usano solo gli atomi e le informazioni di connessione per il calcolo.
# i3D. Internal 3D descriptors usano informazioni sulle coordinate di ciascuna molecola; comunque, non cambiano ruotando o traslando la conformazione.
# x3D. External 3D descriptors usano le coordinate 3D ma richiedono un unico 'frame' di riferimento (ad esempio ligandi dockati allo stesso recettore)
All'interno di queste classi poi ci sono descrittori che sono ciascuno identificato da un nome.
Come da immagine:
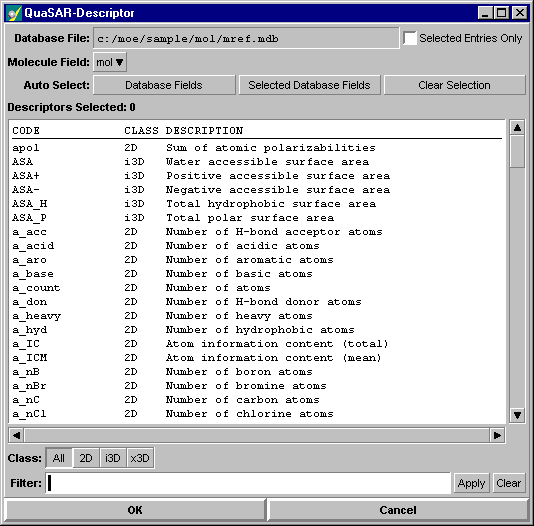
- # In particolare i Descrittori 2D si occupano di
- Physical Properties
Propriet� fisiche che possono essere calcolate dalla tabella di connessione tra gli atomi di una molecola
Es: Il momento di dipolo, il potenziale di ionizzazione, l'energia elettronica, van der Waals volume, ...
- Subdivided Surface Areas
The Subdivided Surface Areas are descriptors based on an approximate accessible van der Waals surface area calculation for each atom, vi along with some other atomic property, pi. The vi are calculated using a connection table approximation. Each descriptor in a series is defined to be the sum of the vi over all atoms i such that pi is in a specified range (a,b].
- Atom Counts and Bond Counts
The atom count and bond count descriptors are functions of the counts of atoms and bonds (subdivided according to various criteria). [*/]
- Kier&Hall Connectivity and Kappa Shape Indices
- Adjacency and Distance Matrix Descriptors
- Pharmacophore Feature Descriptors
- Partial Charge Descriptors
- # I descrittori molecolari 3D
- Potential Energy Descriptors
- Surface Area, Volume and Shape Descriptors
[*] Conformation Dependent Charge Descriptors
Ulteriori informazioni sul sito di ProChem. |
MolecularLab.it - Animazioni, News, didattica & Community su bioinformatica, biologia molecolare ed ingegneria genetica.
BUONE REGOLE DEL FORUM:
- Prima di postare qualunque cosa leggere il Regolamento!
- Hai provato a cercare prima di postare il tuo problema? |
 |
|
|
kORdA
Utente Attivo
  

Prov.: Milano
Citt�: Monza

1303 Messaggi |
 Inserito il - 31 ottobre 2006 : 13:50:24 Inserito il - 31 ottobre 2006 : 13:50:24





|
ah, ma quelli sono descrittori QSAR (i quantomeccanici rappresentano solo un gruppo di tutti i descrittori disponibili).
a proposito, Atreliu: se ne hai dimestichezza mi potresti spiegare se esiste un modo (attraverso quei descrittori) per monitorare l'esistenza di legame H tra due partner (coppia di atomi accettore/donatore) per tutto il tempo di una dinamica molecolare (partendo, ad es., da un database MDB)
|
http://www.linkedin.com/in/dariocorrada |
 |
|
| |
Discussione |
|
|
|
Quanto � utile/interessante questa discussione:
| MolecularLab.it |
© 2003-24 MolecularLab.it |
 |
|
|





