Quanto � utile/interessante questa discussione:
| Autore |
Discussione |
|
|
Donde
Utente Junior



272 Messaggi |
 Inserito il - 13 giugno 2011 : 22:00:36 Inserito il - 13 giugno 2011 : 22:00:36





|
ciao, conoscete un programma per windows, possibilmente semplice da usare, che possa analizzare una fotografia e calcolare la percentuale della superficie occupata dalle cellule cresciute su una piastra?
di seguito riporto un esempio di immagine da analizzare:
http://imageshack.us/photo/my-images/28/dscn2181yb.jpg/
grazie mille 
|
"DNA just is. And we dance to its music." |
|
|
|
|
chick80
Moderatore
    

Citt�: Edinburgh

11491 Messaggi |
 Inserito il - 13 giugno 2011 : 23:36:39 Inserito il - 13 giugno 2011 : 23:36:39




|
Premessa: se riuscissi a fare un'immagine in fluorescenza o almeno fare una controcolorazione (es. blu di toluidina, cristal violetto, qualcosa del genere) il risultato sarebbe decisamente migliore. Ad ogni modo qualcosa si pu� fare facilmente con ImageJ.
Ti spiego la procedura generale, ma dovrai giocare un po' con i valori.
IMPORTANTE: io uso la versione di ImageJ di MacBioPhotonics ( http://www.macbiophotonics.ca/downloads.htm ) che ha molti plugins aggiuntivi. Alcuni dei comandi che user� non li troverai nella versione vanilla di ImageJ.
1) Apri l'immagine
2) Convertila in 8-bit (Image->Type->8-bit)
3) Aumenta il contrasto dell'immagine. Process->Enhance contrast. Un valore di ~2% sembra andare bene, clicca "Normalize histogram".
Otterrai qualcosa di questo tipo:
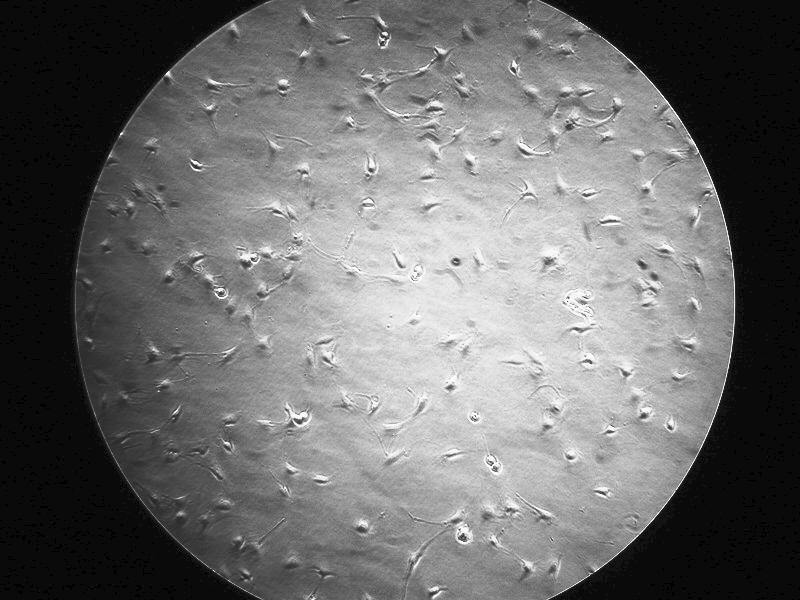
4) Ora dobbiamo "binarizzare" l'immagine, convertendola in un'immagine bianca dove ci sono le cellule e nera dove non ci sono. Se avessi una controcolorazione probabilmente si riuscirebbe a farlo con lo strumento Threshold o Color Threshold (menu Image->Adjust) Qui il contrasto � troppo basso ed inoltre il centro dell'immagine � pi� luminoso dei bordi (il diaframma del microscopio � completamente aperto?), quindi dobbiamo usare un thresholding locale. Plugins->Segmentation ne contiene diversi.
Io ho usato Local Treshold e ho settato il raggio a 15px e i limiti a -163 e -19 (aggiustali fino a quando non copri che le cellule)
Deseleziona "Set background pixel to NA".
5) Binarizza l'immagine con Process->Binary->Make Binary. Binary->Fill Holes e Binary->Close possono migliorare la qualit� dell'immagine.
A questo punto avrai qualcosa di questo tipo

6) Ora puoi passare alla detezione delle cellule.
Prima di lanciarlo scegli per� i parametri che vuoi misurare con Analyze->Set Measurement. Ad es. puoi scegliere Area Fraction, Size etc.
Ora lancia l'analisi con Analyze->analyze particles.
Io ho usato size 30-500, circularity 0.0-1.0. Scegli Display results e Summarize. Se il risultato non � corretto rifai "Analyze Particles", ma scegli anche "Clear results" per eliminare i risultati di prima.
Nel summary avrai i risultati richiesti. Nota che se vuoi la frazione di area occupata dovrai lanciare l'analisi delle particelle solo sull'area del campo visivo del microscopio, quindi prima di lanciare Analyze particles dovrai usare lo strumento Cerchio per selezionare il campo visivo.
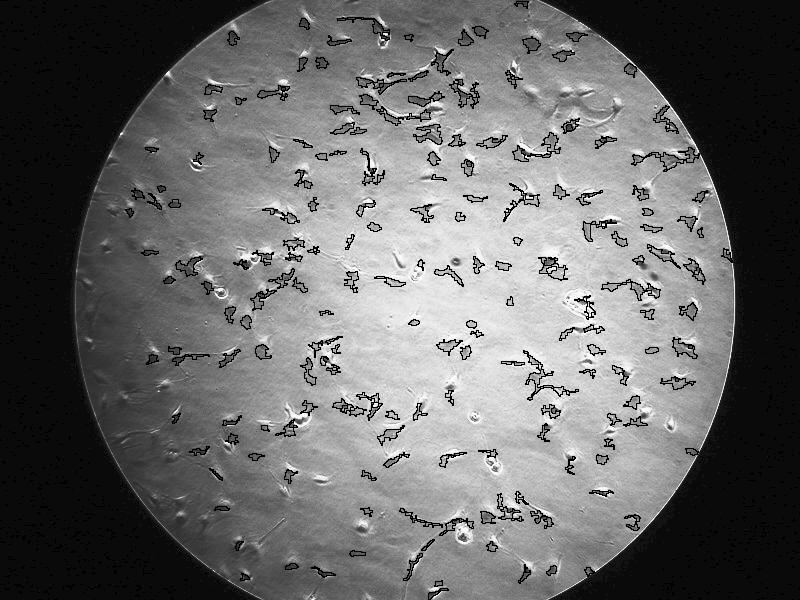
Ecco il risultato che ho ottenuto, ed un overlay con l'immagine originale.
Come vedi il risultato � OK in alcune parti, ma decisamente non ottimale in generale. Come gi� detto all'inizio, una controcolorazione pu� aiutare enormemente. Inoltre conta che non sono stato troppo a giocare con i parametri.

 |
Sei un nuovo arrivato?
Leggi il regolamento del forum e presentati qui
My photo portfolio (now on G+!) |
 |
|
|
Donde
Utente Junior



272 Messaggi |
 Inserito il - 14 giugno 2011 : 16:28:18 Inserito il - 14 giugno 2011 : 16:28:18





|
grazie mille chick, non potevi darmi una risposta pi� esaustiva e dettagliata di cos�!  allora cerco di ottenere fotografie con un contrasto maggiore (purtroppo anche quel microscopio ha un po' di problemi e non aiuta..) e poi provo ad usare quel programma. allora cerco di ottenere fotografie con un contrasto maggiore (purtroppo anche quel microscopio ha un po' di problemi e non aiuta..) e poi provo ad usare quel programma. |
"DNA just is. And we dance to its music." |
 |
|
| |
Discussione |
|
|
|
Quanto � utile/interessante questa discussione:
| MolecularLab.it |
© 2003-18 MolecularLab.it |
 |
|
|









