| Autore |
Discussione |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 17 maggio 2016 : 16:56:34 Inserito il - 17 maggio 2016 : 16:56:34



|
Ciao a tutti, ho difficolt� a capire come svolgere quest'esercizio, vi chiedo aiuto.
Si tratta della segregazione di una malattia autosomica dominante.
� riportata per ogni soggetto la caratterizzazione per un locus VNTR che ha il 2% di ricombinazione con il locus della malattia.
-Calcolare la probabilit� dei nascituri di ereditare la malattia
-Disegnare le regioni cromosomiche con i due loci per tutti gli individui
Non riesco a caricare il pedigree (error500), quindi cerco di scrivervelo:
I- 1/2 m + 1/4 f (affetta)(deceduta)
II- 1/1 m (figlio di I-1+I-2)(affetto) + 2/3 f
III- 1/2 m (affetto)(figlio di II-1+II-2) + 3/4 f
IV- 2/3 f + 2/4 m (affetto)(figlio di III-1+III-2), 2/4 f (figlia di III-1+III-2)+1/2 m
V- 2/2 x (figlio/a di IV-1+IV-2), 1/2 x (figlio/a di IV-3+IV-4)
Spero di essere stato abbastanza chiaro,
grazie
EDIT: Pedigree aggiunto
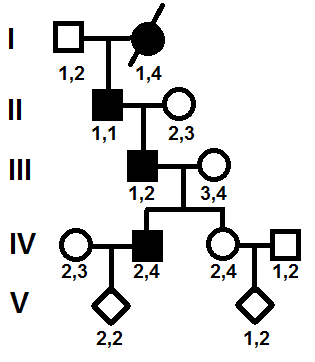
|
|
|
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 17 maggio 2016 : 18:35:40 Inserito il - 17 maggio 2016 : 18:35:40





|
Ho aggiunto il pedigree secondo le tue indicazioni (se ci sono errori fammelo sapere che correggo).
Inizia con la seconda domanda, inizia a disegnare i cromosomi di ciascun individuo e vedere con che allele segrega la malattia.
Se hai problemi, scrivi quali sono e cerchiamo di risolverli assieme. |
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 17 maggio 2016 : 20:26:50 Inserito il - 17 maggio 2016 : 20:26:50



|
Grazie per la tempestivit�.
Ho proprio difficolt� a capire come impostare l'esercizio. Anche nel disegnare i cromosomi non so che metodo/criterio seguire.  
Magari potete rimandarmi a una spiegazione teorica (non ne ho trovate) prima, e cerco di capirci qualcosa. |
 |
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 18 maggio 2016 : 16:19:22 Inserito il - 18 maggio 2016 : 16:19:22





|
Ti faccio l'esempio per la prima generazione, poi continua tu:
I-1: non presenta la malattia quindi sar� omozigote per l'allele recessivo (m)
1-| |-2
| |
m-| |-m
I-2: presenta la malattia quindi avr� l'allele dominate (M) ma non sai a quale dei due alleli del VNTR (1 e 4) � associato, hai due possibilit�:
1-| |-4 1-| |-4
| | | |
m-| |-M M-| |-m
poi guardando il figlio II-1 capisci com'� l'associazione nel genitore.
Prova a disegnarti tutti i cromosomi degli individui dell'albero.
N.B. dato che nel forum non � facile mantenere la formattazione del testo (anche se le indicazioni su come fare le trovi qui: http://www.molecularlab.it/forum/faq.asp#format), dopo che ti sei fatto il tuo schemino a mano, riportali pure scrivendoli cos�:
I-1: 1m/2m
I-2: 1m/4M o 1M/4m |
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 18 maggio 2016 : 16:36:26 Inserito il - 18 maggio 2016 : 16:36:26



|
Ok, ho provato. Pensavo fosse peggio, ma potrebbero esserci errori.
I-1: 1m/2m , I-2: 1M/4m
II-1: 1m/1M , II-2: 2m/3m
III-1: 1M/2m , III-2: 3m/4m
IV-1: 2m/3m , IV-2: 2M/4m , IV-3: 2m/4m , IV-4: 1m/2m
V-1: 2m/2M , V-2: 1m/2m
edit: se non sbaglio, nella trasmissione da III-1 a IV-2 � successo qualcosa durante la segregazione..  |
 |
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 18 maggio 2016 : 17:30:25 Inserito il - 18 maggio 2016 : 17:30:25





|
Citazione:
Messaggio inserito da brunoliegi
Ok, ho provato. Pensavo fosse peggio, ma potrebbero esserci errori.
S�, sembra difficile, ma in realt� non lo �! 
Citazione:
I-1: 1m/2m , I-2: 1M/4m
II-1: 1m/1M , II-2: 2m/3m
III-1: 1M/2m , III-2: 3m/4m
IV-1: 2m/3m , IV-2: 2M/4m , IV-3: 2m/4m , IV-4: 1m/2m
Fino a qui OK!
Citazione:
V-1: 2m/2M , V-2: 1m/2m
Per la generazione V in realt� non sai ancora se i feti sono sani o malati (� quello che ti viene chiesto), quindi non puoi ancora segnare come sono i cromosomi.
Citazione:
edit: se non sbaglio, nella trasmissione da III-1 a IV-2 � successo qualcosa durante la segregazione.. 
S�, ma "che cosa?"
|
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 18 maggio 2016 : 17:32:21 Inserito il - 18 maggio 2016 : 17:32:21



|
Citazione:
S�, ma "che cosa?"
crossing over?  |
 |
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 18 maggio 2016 : 18:05:22 Inserito il - 18 maggio 2016 : 18:05:22





|
Esatto! 
Quindi ora avresti tutti gli elementi per rispondere alla prima domanda:
"-Calcolare la probabilit� dei nascituri di ereditare la malattia" |
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 18 maggio 2016 : 18:10:01 Inserito il - 18 maggio 2016 : 18:10:01



|
Citazione:
Messaggio inserito da GFPina
Quindi ora avresti tutti gli elementi per rispondere alla prima domanda:
"-Calcolare la probabilit� dei nascituri di ereditare la malattia"
E come si fa? Cio� non capisco quel 2% di ricombinazione come considerarlo..
La mia testa al momento mi dice che il primo � al 100% malato e il secondo sicuramente sano, ma so che c'� qualcosa che non va..   |
 |
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 18 maggio 2016 : 18:36:38 Inserito il - 18 maggio 2016 : 18:36:38





|
Prendiamo il primo caso (primo feto).
Il genitore che presenta la malattia �
IV-2: 2M/4m
2-| |-4
| |
M-| |-m
questo individuo che gameti potr� produrre e in che frequenza? |
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 18 maggio 2016 : 18:40:31 Inserito il - 18 maggio 2016 : 18:40:31



|
Citazione:
Messaggio inserito da GFPina
Prendiamo il primo caso (primo feto).
Il genitore che presenta la malattia �
IV-2: 2M/4m
2-| |-4
| |
M-| |-m
questo individuo che gameti potr� produrre e in che frequenza?
1/2 M e 1/2 m |
 |
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 18 maggio 2016 : 19:12:55 Inserito il - 18 maggio 2016 : 19:12:55





|
Citazione:
1/2 M e 1/2 m
Scusa, non ho capito!
con "1/2" intendi "un mezzo"? Non i marcatori del VNTR? Che sarebbero in questo caso 2 e 4.
Se s�, perch� i marcatori del VNTR sono spariti nei gameti che indichi?
Altrimenti la tua soluzione andrebbe bene per un albero genealogico dove � indicata solo la malattia e non i polimorfismi, avresti un padre (IV-2) affetto, che ha ovviamente il 50% di probabilit� di trasmettere la patologia al figlio.
Ma qua hai anche gli alleli del VNTR che ti danno un'indicazione in pi�.
Quindi, ripeto la mia domanda:
Citazione:
Messaggio inserito da GFPina
IV-2: 2M/4m
2-| |-4
| |
M-| |-m
questo individuo che gameti potr� produrre e in che frequenza?
Aiutino: il 2% non � messo a caso, in qualche modo lo devi utilizzare! |
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 18 maggio 2016 : 20:53:43 Inserito il - 18 maggio 2016 : 20:53:43



|
S�, intendevo 50 e 50 (sapendo inconsciamente di sbagliare).
Provo a buttarmi: devo moltiplicare il 2% per il 50% di probabilit� di trasmettere la patologia?  
No, non riesco ad arrivare ad una soluzione decente. |
 |
|
|
brunoliegi
Nuovo Arrivato

11 Messaggi |
 Inserito il - 19 maggio 2016 : 10:52:59 Inserito il - 19 maggio 2016 : 10:52:59



|
Forse alla fine ho capito (ragionando sui gameti e sulla % di ricombinazione):
V-1 sar� affetto dalla patologia con una probabilit� del 98%.
V-2 sar� affetto dalla patologia con una probabilit� dello 0% (sicuramente sano).
Nel padre di V-1 potrebbe esserci ricombinazione, mentre la madre � un omozigote rec.
I genitori di V-2 sono omozigoti rec, quindi la ricombinazione non cambia le probabilit�. |
 |
|
|
GFPina
Moderatore
    

Citt�: Milano

8408 Messaggi |
 Inserito il - 23 maggio 2016 : 16:12:12 Inserito il - 23 maggio 2016 : 16:12:12





|
Scusa ti avevo risposto venerd�, ma vedo ora che non risulta la mia risposta.
Comunque � giusto! 
L'unica cosa � che cambierei questa frase: "I genitori di V-2 sono omozigoti rec, quindi la ricombinazione non cambia le probabilit�."
con "I genitori di V-2 sono omozigoti rec, quindi non possono trasmettere la patologia."
La ricombinazione "non cambierebbe la P" se avessi un genitore affetto, ma omozigote per gli alleli RFLP. |
 |
|
| |
Discussione |
|











