Quanto � utile/interessante questa discussione:
| Autore |
Discussione |
|
|
Giuliano652
Moderatore
   

Prov.: Brescia

6942 Messaggi |
 Inserito il - 19 febbraio 2013 : 11:37:38 Inserito il - 19 febbraio 2013 : 11:37:38




|
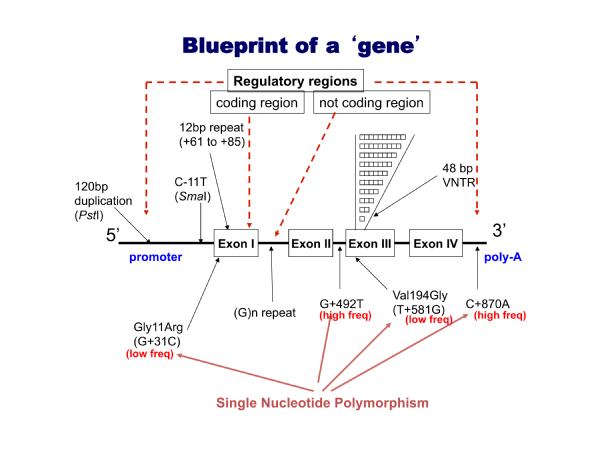
Ho scoperto che ho un programma brevissimo per un esame e provo a darlo, ma gi� alla seconda slide, non avendo seguito il corso, ho difficolt� interpretative, credo sia l'immagine di tutto quello che � possibile trovare in un gene. La slide la metto in allegato.
Immagine:
313,45�KB
La mia interpretazione di questa slide � questa:
al 5' c'� il promotore
al 3' il polyA
120bp duplication (PstI) sul promotore non la capisco
C-11T (small) c'� una mutazione che cambia C in T in posizione 11 prima dell'inizio di trascrizione, giusto? E (small)?
esoni e introni � chiaro
12bp repeat (+61 to +85) abbiamo la possibilit� di trovare una ripetizione di 12bp in quella posizione. E questo che informazione mi d�?
Gly11Arg (G+31C) low freq capisco questo: Glicina diventa Arginina in posizione 11 (undicesimo codone?) G+31C c'� una G che muta in C in posizione 31? Comunque, visto che � su un esone, la frequenza di mutazione � bassa
(G)n repeat ovvero � possibile trovare in un introne una sequenza di G, corretto? E questo che informazioni mi d�?
G+492T high freq ovvero c'� una mutazione da G a T in posizione 492 ed � ad alta frequenza essendo in un introne
48bp VNTR mi fa vedere che � possibile trovare in un esone una zona VNTR con ripetizioni pi� o meno lunghe, giusto?
|
Uno strumento utile per l'utilizzo del forum: cerca
Se sei nuovo leggi il regolamento e, se vuoi farti conoscere, presentati qui
Link utili alla professione:
FAQ su nutrizione e dietistica
[Raccolta link] cosa bisogna sapere del lavoro del biologo
Burocrazia per lavorare come biologi
D� pi� sbocchi biologia delle posidonie o biotech suine?
|
|
|
|
|
Geeko
Utente
 
Citt�: Milano

1043 Messaggi |
 Inserito il - 19 febbraio 2013 : 12:36:24 Inserito il - 19 febbraio 2013 : 12:36:24




|
Eh di fatti cos� senza altre info � difficile interpretare tutto.
Comunque s�, quelli indicati sotto sono tutti SNPs annotati nel gene in questione e infatti la frequenza con cui avvengono nelle porzioni esoniche � indicata con "low" e questo suggerisce che questi polimorfismi non lasciano completamente inalterata la funzione della proteina (ma qui bisognerebbe contestualizzare il tutto).
L'indicazione C-11T corrisponde a una transizione C->T che avviene in posizione -11. (SmaI) indica che questa transizione fa comparire un sito di riconoscimento per l'enzima di restrizione SmaI (potrebbe essere un RFLP).
Poi ad esempio come dicevi Gly11Arg(G+31C) corrisponde ad un SNP in cui una transversione G->C nella prima posizione dell'undicesimo codone ha sostituito una glicina con un'arginina (ad esempio GGU->CGU). |

|
 |
|
|
Giuliano652
Moderatore
   

Prov.: Brescia

6942 Messaggi |
|
| |
Discussione |
|
|
|
Quanto � utile/interessante questa discussione:
| MolecularLab.it |
© 2003-24 MolecularLab.it |
 |
|
|






